渔业研究 ›› 2023, Vol. 45 ›› Issue (3): 233-245.DOI: 10.14012/j.cnki.fjsc.2023.03.003
廖梦香( )
)
收稿日期:2023-03-27
出版日期:2023-06-25
发布日期:2023-06-16
作者简介:廖梦香(1990—)女,助理农艺师,硕士,研究方向为水产养殖与遗传育种研究。E-mail:360878796@qq.com
基金资助:Received:2023-03-27
Online:2023-06-25
Published:2023-06-16
摘要:
为探究闽江不同河段河蚬的形态学和线粒体基因遗传多样性,本研究在闽江的6个不同河段[延平(YP)、闽侯(MH)、龙祥岛(LXD)、马尾(MW)、长乐(CL)和连江(LJ)]共随机采集180个河蚬样品,测量和分析其形态学数据,并以线粒体COⅠ、Cyt b和16S rRNA基因部分序列作为分子标记,进行PCR扩增与测序分析。结果显示:闽江6个不同河段河蚬壳长、壳高和壳宽的变异系数较小,而软体重、壳重和总重的变异系数较大,其中软体重的变异系数最大的群体为LJ(53.30%)。获得线粒体COⅠ、Cyt b和16S rRNA基因序列片段长度分别为444、466、364 bp,3个基因中A+T含量相近且明显高于C+G的含量;COⅠ和Cyt b基因的单倍型数量明显多于16S rRNA基因;COⅠ和Cyt b基因的遗传多样性比16S rRNA基因高;系统进化树显示,3个基因片段的进化速度:COⅠ>Cyt b>16S rRNA;中性检验和岐点分布图结果表明,闽江河蚬群体很稳定,均未发生过大规模的种群扩张等历史事件。综上所述,闽江6个河段河蚬在形态上没有存在显著的差异,河蚬的COⅠ、Cyt b比16S rRNA基因遗传多样性更高、进化速度更快,即使分化出独立的遗传群体,也未发生过大规模的种群扩张等历史事件,可作为一个整体进行保护和开发应用。
中图分类号:
廖梦香. 闽江不同河段河蚬的形态学及遗传多样性比较分析[J]. 渔业研究, 2023, 45(3): 233-245.
LIAO Mengxiang. Comparative analysis of morphological and genetic diversity of Corbicula fluminea in different reaches of Minjiang River[J]. Journal of Fisheries Research, 2023, 45(3): 233-245.
| 基因Gene | 引物序列(5’-3’) Primer sequence (5’-3’) | 序列登记号GenBank |
|---|---|---|
| COⅠ | F:GCTATTCCAGGGACTTTACTA R:CCAGCTAACACAGGCATT | AY097303.1 |
| Cyt b | F:TTATAGGGTCGGCAGGAA R:GCATATTGGTCGTGGTATT | MG546300.1 |
| 16S rRNA | F:TTAACGGCTGCGATTGAA R:CGAACAGTCCTACTATTATACC | NC_046410.1:4439~5453 |
表1 引物信息
Tab.1 Primer information
| 基因Gene | 引物序列(5’-3’) Primer sequence (5’-3’) | 序列登记号GenBank |
|---|---|---|
| COⅠ | F:GCTATTCCAGGGACTTTACTA R:CCAGCTAACACAGGCATT | AY097303.1 |
| Cyt b | F:TTATAGGGTCGGCAGGAA R:GCATATTGGTCGTGGTATT | MG546300.1 |
| 16S rRNA | F:TTAACGGCTGCGATTGAA R:CGAACAGTCCTACTATTATACC | NC_046410.1:4439~5453 |
| 基因Gene | 预变性 Predenaturation | 单循环步骤Single cycle step | 循环次数 Cycles | 后延伸 Posterior extension | ||
|---|---|---|---|---|---|---|
| 变性Denaturation | 退火Annealing | 延伸Extension | ||||
| COⅠ | 94℃,5 min | 94℃,30 s | 55℃,45 s | 72℃,45 s | 35 | 72℃,10 min |
| Cyt b | 53℃,45 s | |||||
| 16S rRNA | 52℃,30 s | |||||
表2 PCR扩增程序
Tab.2 PCR amplification program
| 基因Gene | 预变性 Predenaturation | 单循环步骤Single cycle step | 循环次数 Cycles | 后延伸 Posterior extension | ||
|---|---|---|---|---|---|---|
| 变性Denaturation | 退火Annealing | 延伸Extension | ||||
| COⅠ | 94℃,5 min | 94℃,30 s | 55℃,45 s | 72℃,45 s | 35 | 72℃,10 min |
| Cyt b | 53℃,45 s | |||||
| 16S rRNA | 52℃,30 s | |||||
| 性状 Traits | 延平YP | 闽侯MH | 龙祥岛LXD | 马尾MW | 长乐CL | 连江LJ | ||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | |
| 壳长/mm SL | 19.32±2.85 | 14.76 | 19.68±1.48 | 7.51 | 21.27±2.13 | 10.018 | 21.41±3.62 | 16.92 | 19.98±3.38 | 16.90 | 18.02±2.66 | 14.78 |
| 壳高/mm SH | 17.46±2.16 | 12.38 | 18.23±1.50 | 8.24 | 19.90±2.13 | 10.679 | 19.40±3.23 | 16.64 | 18.04±2.54 | 14.06 | 16.67±2.66 | 15.95 |
| 壳宽/mm SW | 11.46±1.28 | 11.150 | 12.29±1.01 | 8.25 | 13.09±1.15 | 8.804 | 12.70±1.83 | 14.37 | 12.58±1.37 | 10.86 | 11.80±1.72 | 14.56 |
| 软体重/g SBW | 0.43±0.18 | 42.66 | 0.43±0.11 | 25.18 | 0.60±0.16 | 27.215 | 0.79±0.41 | 52.59 | 0.55±0.29 | 52.78 | 0.56±0.30 | 53.30 |
| 壳重/g SW | 1.50±0.48 | 32.16 | 1.76±0.45 | 25.77 | 2.29±0.58 | 25.335 | 2.09±1.02 | 48.82 | 1.88±0.61 | 32.28 | 1.64±0.71 | 43.03 |
| 总重/g TW | 2.47±0.80 | 32.29 | 2.83±0.67 | 23.76 | 3.62±0.93 | 25.582 | 3.42±1.70 | 49.82 | 3.04±1.13 | 37.04 | 2.51±1.11 | 44.13 |
| 壳高/壳长 SH/SL | 0.91±0.06a | 6.60 | 0.93±0.04ab | 3.99 | 0.94±0.03b | 2.834 | 0.91±0.06a | 6.17 | 0.91±0.04a | 4.71 | 0.92±0.03ab | 2.97 |
| 壳宽/壳长 SW/SL | 0.60±0.07a | 12.24 | 0.63±0.03b | 4.99 | 0.62±0.03ab | 5.043 | 0.60±0.04a | 6.49 | 0.64±0.05bc | 8.33 | 0.66±0.03c | 4.28 |
| 软体重/总重 SBW/TW | 0.17±0.03b | 19.03 | 0.15±0.02a | 9.86 | 0.17±0.02ab | 13.102 | 0.23±0.04c | 17.93 | 0.17±0.04b | 21.64 | 0.22±0.04c | 16.28 |
| 壳重/总重 SW/TW | 0.61±0.07a | 11.82 | 0.62±0.042a | 6.760 | 0.63±0.03ab | 3.897 | 0.61±0.07a | 10.95 | 0.63±0.05a | 8.07 | 0.66±0.03b | 5.09 |
表3 闽江6个河段河蚬群体的形态学性状统计量(n=180)
Tab.3 Morphological traits statistics of C.fluminea populations in the 6 reachs of Minjiang River (n=180)
| 性状 Traits | 延平YP | 闽侯MH | 龙祥岛LXD | 马尾MW | 长乐CL | 连江LJ | ||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | 平均值± 标准差 Mean±SD | 变异 系数/% CV | |
| 壳长/mm SL | 19.32±2.85 | 14.76 | 19.68±1.48 | 7.51 | 21.27±2.13 | 10.018 | 21.41±3.62 | 16.92 | 19.98±3.38 | 16.90 | 18.02±2.66 | 14.78 |
| 壳高/mm SH | 17.46±2.16 | 12.38 | 18.23±1.50 | 8.24 | 19.90±2.13 | 10.679 | 19.40±3.23 | 16.64 | 18.04±2.54 | 14.06 | 16.67±2.66 | 15.95 |
| 壳宽/mm SW | 11.46±1.28 | 11.150 | 12.29±1.01 | 8.25 | 13.09±1.15 | 8.804 | 12.70±1.83 | 14.37 | 12.58±1.37 | 10.86 | 11.80±1.72 | 14.56 |
| 软体重/g SBW | 0.43±0.18 | 42.66 | 0.43±0.11 | 25.18 | 0.60±0.16 | 27.215 | 0.79±0.41 | 52.59 | 0.55±0.29 | 52.78 | 0.56±0.30 | 53.30 |
| 壳重/g SW | 1.50±0.48 | 32.16 | 1.76±0.45 | 25.77 | 2.29±0.58 | 25.335 | 2.09±1.02 | 48.82 | 1.88±0.61 | 32.28 | 1.64±0.71 | 43.03 |
| 总重/g TW | 2.47±0.80 | 32.29 | 2.83±0.67 | 23.76 | 3.62±0.93 | 25.582 | 3.42±1.70 | 49.82 | 3.04±1.13 | 37.04 | 2.51±1.11 | 44.13 |
| 壳高/壳长 SH/SL | 0.91±0.06a | 6.60 | 0.93±0.04ab | 3.99 | 0.94±0.03b | 2.834 | 0.91±0.06a | 6.17 | 0.91±0.04a | 4.71 | 0.92±0.03ab | 2.97 |
| 壳宽/壳长 SW/SL | 0.60±0.07a | 12.24 | 0.63±0.03b | 4.99 | 0.62±0.03ab | 5.043 | 0.60±0.04a | 6.49 | 0.64±0.05bc | 8.33 | 0.66±0.03c | 4.28 |
| 软体重/总重 SBW/TW | 0.17±0.03b | 19.03 | 0.15±0.02a | 9.86 | 0.17±0.02ab | 13.102 | 0.23±0.04c | 17.93 | 0.17±0.04b | 21.64 | 0.22±0.04c | 16.28 |
| 壳重/总重 SW/TW | 0.61±0.07a | 11.82 | 0.62±0.042a | 6.760 | 0.63±0.03ab | 3.897 | 0.61±0.07a | 10.95 | 0.63±0.05a | 8.07 | 0.66±0.03b | 5.09 |
| 基因 Gene | 群体 Population | 碱基组成/% Base composition | ||||||
|---|---|---|---|---|---|---|---|---|
| A | C | T | G | A+T | C+G | |||
| COⅠ | 延平 | 36.1 | 18.0 | 29.6 | 16.2 | 65.7 | 34.2 | |
| 闽侯 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 龙祥岛 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 马尾 | 32.6 | 17.3 | 32.7 | 17.4 | 65.3 | 34.7 | ||
| 长乐 | 31.2 | 16.6 | 34.6 | 17.6 | 65.8 | 34.2 | ||
| 连江 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 平均 | 32.3 | 16.9 | 33.5 | 17.3 | 65.8 | 34.2 | ||
| Cyt b | 延平 | 29.0 | 11.4 | 42.1 | 17.5 | 71.1 | 28.9 | |
| 闽侯 | 39.1 | 15.7 | 32.6 | 12.6 | 71.7 | 28.3 | ||
| 龙祥岛 | 40.7 | 16.5 | 30.9 | 11.9 | 71.6 | 28.4 | ||
| 马尾 | 45.4 | 19.3 | 25.5 | 9.8 | 70.9 | 29.1 | ||
| 长乐 | 42.2 | 17.6 | 29.0 | 11.3 | 71.2 | 28.9 | ||
| 连江 | 39.1 | 15.7 | 32.5 | 12.6 | 71.6 | 28.3 | ||
| 平均 | 39.3 | 16.0 | 32.1 | 12.6 | 71.4 | 28.6 | ||
| 16S rRNA | 延平 | 35.3 | 13.6 | 33.9 | 17.1 | 69.2 | 30.7 | |
| 闽侯 | 34.1 | 16.3 | 34.8 | 14.8 | 68.9 | 31.1 | ||
| 龙祥岛 | 34.3 | 16.0 | 34.6 | 15.1 | 68.9 | 31.1 | ||
| 马尾 | 35.0 | 14.5 | 34.2 | 16.3 | 69.2 | 30.8 | ||
| 长乐 | 34.6 | 15.3 | 34.6 | 15.5 | 69.2 | 30.8 | ||
| 连江 | 34.5 | 15.4 | 34.5 | 15.6 | 69.0 | 31.0 | ||
| 平均 | 34.6 | 15.2 | 34.4 | 15.7 | 69.1 | 30.9 | ||
表4 闽江6个河段河蚬群体COⅠ、Cyt b和16S rRNA基因碱基组成
Tab.4 The base composition of COⅠ,Cyt b and 16S rRNA gene fragments of C.fluminea populations in the 6 reachs of Minjiang River
| 基因 Gene | 群体 Population | 碱基组成/% Base composition | ||||||
|---|---|---|---|---|---|---|---|---|
| A | C | T | G | A+T | C+G | |||
| COⅠ | 延平 | 36.1 | 18.0 | 29.6 | 16.2 | 65.7 | 34.2 | |
| 闽侯 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 龙祥岛 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 马尾 | 32.6 | 17.3 | 32.7 | 17.4 | 65.3 | 34.7 | ||
| 长乐 | 31.2 | 16.6 | 34.6 | 17.6 | 65.8 | 34.2 | ||
| 连江 | 31.2 | 16.5 | 34.6 | 17.6 | 65.8 | 34.1 | ||
| 平均 | 32.3 | 16.9 | 33.5 | 17.3 | 65.8 | 34.2 | ||
| Cyt b | 延平 | 29.0 | 11.4 | 42.1 | 17.5 | 71.1 | 28.9 | |
| 闽侯 | 39.1 | 15.7 | 32.6 | 12.6 | 71.7 | 28.3 | ||
| 龙祥岛 | 40.7 | 16.5 | 30.9 | 11.9 | 71.6 | 28.4 | ||
| 马尾 | 45.4 | 19.3 | 25.5 | 9.8 | 70.9 | 29.1 | ||
| 长乐 | 42.2 | 17.6 | 29.0 | 11.3 | 71.2 | 28.9 | ||
| 连江 | 39.1 | 15.7 | 32.5 | 12.6 | 71.6 | 28.3 | ||
| 平均 | 39.3 | 16.0 | 32.1 | 12.6 | 71.4 | 28.6 | ||
| 16S rRNA | 延平 | 35.3 | 13.6 | 33.9 | 17.1 | 69.2 | 30.7 | |
| 闽侯 | 34.1 | 16.3 | 34.8 | 14.8 | 68.9 | 31.1 | ||
| 龙祥岛 | 34.3 | 16.0 | 34.6 | 15.1 | 68.9 | 31.1 | ||
| 马尾 | 35.0 | 14.5 | 34.2 | 16.3 | 69.2 | 30.8 | ||
| 长乐 | 34.6 | 15.3 | 34.6 | 15.5 | 69.2 | 30.8 | ||
| 连江 | 34.5 | 15.4 | 34.5 | 15.6 | 69.0 | 31.0 | ||
| 平均 | 34.6 | 15.2 | 34.4 | 15.7 | 69.1 | 30.9 | ||
| 基因 Gene | 单倍型 Haplotypes | 延平 YP | 闽侯 MH | 龙祥岛 LXD | 马尾 MW | 长乐 CL | 连江 LJ | 总计 Total | 百分比/% Percentage | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| COⅠ | Hap1 | 4 | 2 | 1 | 7 | 9.7 | ||||||||||||
| Hap2 | 3 | 5 | 3 | 1 | 4 | 16 | 22.2 | |||||||||||
| Hap3 | 3 | 7 | 5 | 2 | 6 | 23 | 31.9 | |||||||||||
| Hap4 | 1 | 2 | 3 | 4.2 | ||||||||||||||
| Hap5 | 1 | 1 | 1.4 | |||||||||||||||
| Hap6 | 1 | 1 | 1.4 | |||||||||||||||
| Hap7 | 1 | 1 | 1.4 | |||||||||||||||
| Hap8 | 1 | 1 | 1.4 | |||||||||||||||
| Hap9 | 1 | 1 | 1.4 | |||||||||||||||
| Hap10 | 2 | 2 | 2.8 | |||||||||||||||
| Hap11 | 1 | 1 | 1.4 | |||||||||||||||
| Hap12 | 1 | 1 | 1.4 | |||||||||||||||
| Hap13 | 3 | 3 | 4.2 | |||||||||||||||
| Hap14 | 1 | 1 | 1.4 | |||||||||||||||
| Hap15 | 1 | 1 | 2 | 2.8 | ||||||||||||||
| Hap16 | 1 | 1 | 1.4 | |||||||||||||||
| Hap17 | 4 | 4 | 5.6 | |||||||||||||||
| Hap18 | 1 | 1 | 1.4 | |||||||||||||||
| Hap19 | 1 | 1 | 1.4 | |||||||||||||||
| Hap20 | 1 | 1 | 1.4 | |||||||||||||||
| 主要单倍型 和占比/% | Hap1 (33.3) | Hap3 (58.3) | Hap3 (41.7) | Hap13 (25.0) | Hap17 (33.3) | Hap3 (50.0) | — | — | ||||||||||
| Cyt b | Ha1 | 4 | 4 | 5.6 | ||||||||||||||
| Ha2 | 4 | 2 | 6 | 8.5 | ||||||||||||||
| Ha3 | 1 | 1 | 1.4 | |||||||||||||||
| Ha4 | 1 | 8 | 9 | 12.7 | ||||||||||||||
| Ha5 | 1 | 3 | 2 | 6 | 8.5 | |||||||||||||
| Ha6 | 8 | 7 | 3 | 18 | 25.4 | |||||||||||||
| Ha7 | 4 | 2 | 3 | 9 | 12.7 | |||||||||||||
| Ha8 | 1 | 1 | 1.4 | |||||||||||||||
| Ha9 | 1 | 1 | 1.4 | |||||||||||||||
| Ha10 | 1 | 1 | 1.4 | |||||||||||||||
| Ha11 | 1 | 1 | 1.4 | |||||||||||||||
| Ha12 | 4 | 4 | 5.6 | |||||||||||||||
| Ha13 | 2 | 2 | 2.8 | |||||||||||||||
| Ha14 | 1 | 1 | 1.4 | |||||||||||||||
| Ha15 | 1 | 1 | 1.4 | |||||||||||||||
| Ha16 | 2 | 2 | 2.8 | |||||||||||||||
| Ha17 | 1 | 1 | 1.4 | |||||||||||||||
| Ha18 | 1 | 1 | 1.4 | |||||||||||||||
| Ha19 | 1 | 1 | 1.4 | |||||||||||||||
| Ha20 | 1 | 1 | 1.4 | |||||||||||||||
| 主要单倍型 和占比/% | Ha1、Ha2 (36.4) | Ha6 (66.7) | Ha6 (58.3) | Ha12 (33.3) | Ha4 (66.7) | Ha6、Ha7 (25.0) | — | — | ||||||||||
| 16S rRNA | H1 | 4 | 4 | 6 | 2 | 16 | 22.5 | |||||||||||
| H2 | 8 | 4 | 6 | 2 | 20 | 28.2 | ||||||||||||
| H3 | 7 | 4 | 4 | 15 | 21.1 | |||||||||||||
| H4 | 5 | 4 | 4 | 13 | 18.3 | |||||||||||||
| H5 | 1 | 1 | 1.4 | |||||||||||||||
| H6 | 1 | 1 | 1.4 | |||||||||||||||
| H7 | 1 | 1 | 1.4 | |||||||||||||||
| H8 | 1 | 1 | 1.4 | |||||||||||||||
| H9 | 3 | 3 | 4.2 | |||||||||||||||
| 主要单倍型 和占比/% | H2 (66.7) | H3 (58.3) | H3、H4 (36.4) | H1、H2 (33.3) | H1、H2 (50.0) | H3、H4 (33.3) | — | — | ||||||||||
表5 闽江6个河段河蚬群体COⅠ、Cyt b和16S rRNA基因单倍型分布
Tab.5 Distribution of COⅠ,Cyt b and 16S rRNA gene haplotypes of C.fluminea populations in the 6 reachs of Minjiang River
| 基因 Gene | 单倍型 Haplotypes | 延平 YP | 闽侯 MH | 龙祥岛 LXD | 马尾 MW | 长乐 CL | 连江 LJ | 总计 Total | 百分比/% Percentage | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| COⅠ | Hap1 | 4 | 2 | 1 | 7 | 9.7 | ||||||||||||
| Hap2 | 3 | 5 | 3 | 1 | 4 | 16 | 22.2 | |||||||||||
| Hap3 | 3 | 7 | 5 | 2 | 6 | 23 | 31.9 | |||||||||||
| Hap4 | 1 | 2 | 3 | 4.2 | ||||||||||||||
| Hap5 | 1 | 1 | 1.4 | |||||||||||||||
| Hap6 | 1 | 1 | 1.4 | |||||||||||||||
| Hap7 | 1 | 1 | 1.4 | |||||||||||||||
| Hap8 | 1 | 1 | 1.4 | |||||||||||||||
| Hap9 | 1 | 1 | 1.4 | |||||||||||||||
| Hap10 | 2 | 2 | 2.8 | |||||||||||||||
| Hap11 | 1 | 1 | 1.4 | |||||||||||||||
| Hap12 | 1 | 1 | 1.4 | |||||||||||||||
| Hap13 | 3 | 3 | 4.2 | |||||||||||||||
| Hap14 | 1 | 1 | 1.4 | |||||||||||||||
| Hap15 | 1 | 1 | 2 | 2.8 | ||||||||||||||
| Hap16 | 1 | 1 | 1.4 | |||||||||||||||
| Hap17 | 4 | 4 | 5.6 | |||||||||||||||
| Hap18 | 1 | 1 | 1.4 | |||||||||||||||
| Hap19 | 1 | 1 | 1.4 | |||||||||||||||
| Hap20 | 1 | 1 | 1.4 | |||||||||||||||
| 主要单倍型 和占比/% | Hap1 (33.3) | Hap3 (58.3) | Hap3 (41.7) | Hap13 (25.0) | Hap17 (33.3) | Hap3 (50.0) | — | — | ||||||||||
| Cyt b | Ha1 | 4 | 4 | 5.6 | ||||||||||||||
| Ha2 | 4 | 2 | 6 | 8.5 | ||||||||||||||
| Ha3 | 1 | 1 | 1.4 | |||||||||||||||
| Ha4 | 1 | 8 | 9 | 12.7 | ||||||||||||||
| Ha5 | 1 | 3 | 2 | 6 | 8.5 | |||||||||||||
| Ha6 | 8 | 7 | 3 | 18 | 25.4 | |||||||||||||
| Ha7 | 4 | 2 | 3 | 9 | 12.7 | |||||||||||||
| Ha8 | 1 | 1 | 1.4 | |||||||||||||||
| Ha9 | 1 | 1 | 1.4 | |||||||||||||||
| Ha10 | 1 | 1 | 1.4 | |||||||||||||||
| Ha11 | 1 | 1 | 1.4 | |||||||||||||||
| Ha12 | 4 | 4 | 5.6 | |||||||||||||||
| Ha13 | 2 | 2 | 2.8 | |||||||||||||||
| Ha14 | 1 | 1 | 1.4 | |||||||||||||||
| Ha15 | 1 | 1 | 1.4 | |||||||||||||||
| Ha16 | 2 | 2 | 2.8 | |||||||||||||||
| Ha17 | 1 | 1 | 1.4 | |||||||||||||||
| Ha18 | 1 | 1 | 1.4 | |||||||||||||||
| Ha19 | 1 | 1 | 1.4 | |||||||||||||||
| Ha20 | 1 | 1 | 1.4 | |||||||||||||||
| 主要单倍型 和占比/% | Ha1、Ha2 (36.4) | Ha6 (66.7) | Ha6 (58.3) | Ha12 (33.3) | Ha4 (66.7) | Ha6、Ha7 (25.0) | — | — | ||||||||||
| 16S rRNA | H1 | 4 | 4 | 6 | 2 | 16 | 22.5 | |||||||||||
| H2 | 8 | 4 | 6 | 2 | 20 | 28.2 | ||||||||||||
| H3 | 7 | 4 | 4 | 15 | 21.1 | |||||||||||||
| H4 | 5 | 4 | 4 | 13 | 18.3 | |||||||||||||
| H5 | 1 | 1 | 1.4 | |||||||||||||||
| H6 | 1 | 1 | 1.4 | |||||||||||||||
| H7 | 1 | 1 | 1.4 | |||||||||||||||
| H8 | 1 | 1 | 1.4 | |||||||||||||||
| H9 | 3 | 3 | 4.2 | |||||||||||||||
| 主要单倍型 和占比/% | H2 (66.7) | H3 (58.3) | H3、H4 (36.4) | H1、H2 (33.3) | H1、H2 (50.0) | H3、H4 (33.3) | — | — | ||||||||||
| 基因 Gene | 群体 Population | 样品数 No.of samples | 单倍型数 No.of haplotypes | 单倍型多样性 Haplotype diversity (Hd±SD) | 核苷酸多样性 Nucleotide diversity (π±SD) | 平均核苷酸差异数 Average number of nucleotide differences (k) |
|---|---|---|---|---|---|---|
| COⅠ | 延平 | 12 | 5 | 0.818±0.070 | 0.303±0.013 | 131.712 |
| 闽侯 | 12 | 2 | 0.530±0.076 | 0.325±0.012 | 141.061 | |
| 龙祥岛 | 12 | 6 | 0.803±0.096 | 0.326±0.012 | 141.364 | |
| 马尾 | 12 | 8 | 0.924±0.057 | 0.341±0.013 | 147.864 | |
| 长乐 | 12 | 7 | 0.879±0.075 | 0.329±0.013 | 142.864 | |
| 连江 | 12 | 4 | 0.682±0.102 | 0.325±0.012 | 141.212 | |
| 合计 | 72 | 20 | 0.840±0.030 | 0.313±0.008 | 136.010 | |
| Cyt b | 延平 | 11 | 5 | 0.782±0.093 | 0.179±0.012 | 76.255 |
| 闽侯 | 12 | 2 | 0.485±0.106 | 0.251±0.012 | 107.152 | |
| 龙祥岛 | 12 | 5 | 0.667±0.141 | 0.213±0.012 | 91.091 | |
| 马尾 | 12 | 6 | 0.848±0.074 | 0.008±0.002 | 3.803 | |
| 长乐 | 12 | 3 | 0.545±0.144 | 0.163±0.012 | 69.455 | |
| 连江 | 12 | 7 | 0.894±0.063 | 0.253±0.012 | 107.985 | |
| 合计 | 71 | 20 | 0.892±0.021 | 0.230±0.001 | 98.330 | |
| 16S rRNA | 延平 | 12 | 2 | 0.485±0.106 | 0.301±0.014 | 103.273 |
| 闽侯 | 12 | 2 | 0.530±0.076 | 0.329±0.014 | 112.955 | |
| 龙祥岛 | 11 | 5 | 0.782±0.093 | 0.339±0.015 | 116.327 | |
| 马尾 | 12 | 4 | 0.773±0.069 | 0.332±0.014 | 113.530 | |
| 长乐 | 12 | 2 | 0.545±0.062 | 0.339±0.014 | 116.182 | |
| 连江 | 12 | 4 | 0.788±0.070 | 0.339±0.014 | 116.424 | |
| 合计 | 71 | 9 | 0.800±0.019 | 0.316±0.009 | 108.212 |
表6 闽江6个河段河蚬群体COⅠ、Cyt b和16S rRNA基因的遗传多样性
Tab.6 Genetic diversity parameters for C.fluminea populations in the 6 reaches of Minjing River based on COⅠ,Cyt b and 16S rRNA gene
| 基因 Gene | 群体 Population | 样品数 No.of samples | 单倍型数 No.of haplotypes | 单倍型多样性 Haplotype diversity (Hd±SD) | 核苷酸多样性 Nucleotide diversity (π±SD) | 平均核苷酸差异数 Average number of nucleotide differences (k) |
|---|---|---|---|---|---|---|
| COⅠ | 延平 | 12 | 5 | 0.818±0.070 | 0.303±0.013 | 131.712 |
| 闽侯 | 12 | 2 | 0.530±0.076 | 0.325±0.012 | 141.061 | |
| 龙祥岛 | 12 | 6 | 0.803±0.096 | 0.326±0.012 | 141.364 | |
| 马尾 | 12 | 8 | 0.924±0.057 | 0.341±0.013 | 147.864 | |
| 长乐 | 12 | 7 | 0.879±0.075 | 0.329±0.013 | 142.864 | |
| 连江 | 12 | 4 | 0.682±0.102 | 0.325±0.012 | 141.212 | |
| 合计 | 72 | 20 | 0.840±0.030 | 0.313±0.008 | 136.010 | |
| Cyt b | 延平 | 11 | 5 | 0.782±0.093 | 0.179±0.012 | 76.255 |
| 闽侯 | 12 | 2 | 0.485±0.106 | 0.251±0.012 | 107.152 | |
| 龙祥岛 | 12 | 5 | 0.667±0.141 | 0.213±0.012 | 91.091 | |
| 马尾 | 12 | 6 | 0.848±0.074 | 0.008±0.002 | 3.803 | |
| 长乐 | 12 | 3 | 0.545±0.144 | 0.163±0.012 | 69.455 | |
| 连江 | 12 | 7 | 0.894±0.063 | 0.253±0.012 | 107.985 | |
| 合计 | 71 | 20 | 0.892±0.021 | 0.230±0.001 | 98.330 | |
| 16S rRNA | 延平 | 12 | 2 | 0.485±0.106 | 0.301±0.014 | 103.273 |
| 闽侯 | 12 | 2 | 0.530±0.076 | 0.329±0.014 | 112.955 | |
| 龙祥岛 | 11 | 5 | 0.782±0.093 | 0.339±0.015 | 116.327 | |
| 马尾 | 12 | 4 | 0.773±0.069 | 0.332±0.014 | 113.530 | |
| 长乐 | 12 | 2 | 0.545±0.062 | 0.339±0.014 | 116.182 | |
| 连江 | 12 | 4 | 0.788±0.070 | 0.339±0.014 | 116.424 | |
| 合计 | 71 | 9 | 0.800±0.019 | 0.316±0.009 | 108.212 |
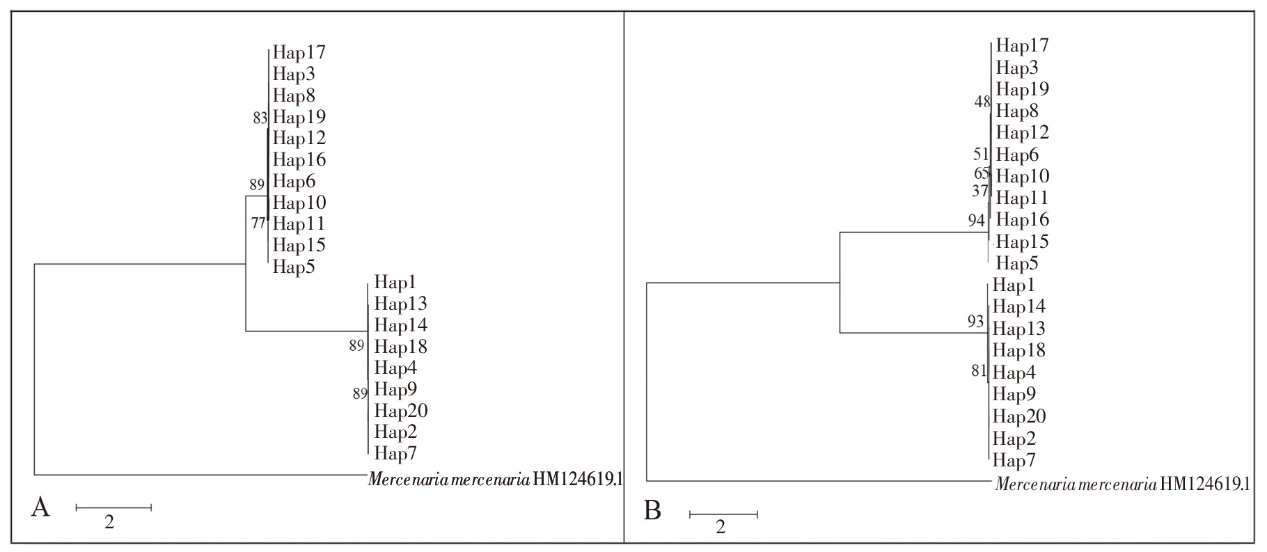
图3 基于闽江6个河段河洁群体COⅠ基因20个单倍型的最大似然树(ML)(A)和邻接树(N-J)(B)
Fig.3 Maximum likelihood(ML) tree (A) and Neighbor-joining (N-J) tree (B) of 20 haplotypes based on partial col gene sequences of C. fluminea populations in the 6 reaches of Minjiang River
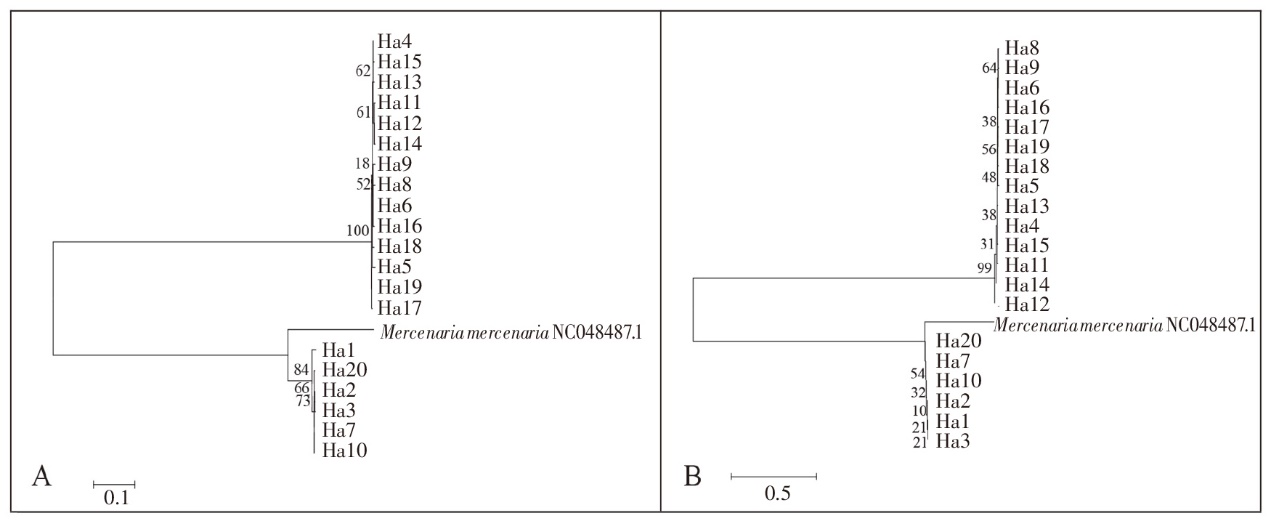
图4 基于闽江6个河段河虮群体Cyt b基因20个单倍型的最大似然树(ML)(A)和邻接树(N-J)(B)
Fig.4 Maximum likelihood (ML) tree(A) and Neighbor-joining (N-J) tree (B) of 20 haplotypes based on partial Cyt b gene sequences of C. fluminea populations in the 6 reaches of Minjiang River
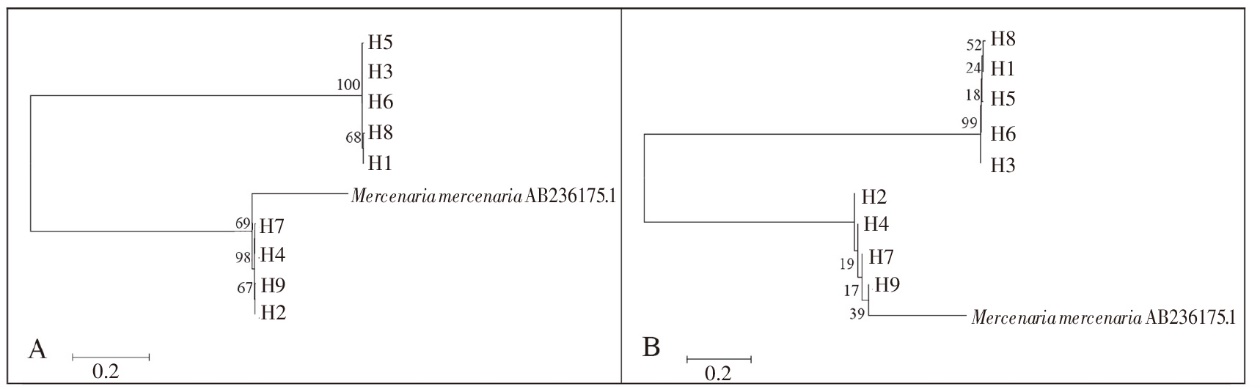
图5 基于闽江6个河段河虮群体16S rRNA基因9个单倍型的最大似然树(ML)(A)和邻接树(N-J)(B)
Fig.5 Maximum likelihood(ML) tree (A) and Neighbor-joining(N-J) tree (B) of 9 haplotypes based on partial 16S rRNA gene sequences of C. fluminea populations in the 6 reaches of Minjiang River
| 基因 Gene | 群体 Population | Tajima’s D | Fu’s Fs | ||
|---|---|---|---|---|---|
| D | P | Fs | P | ||
| COⅠ | 延平 | 1.933 | >0.10 | 21.049 | 0.000 |
| 闽侯 | 2.831 | <0.001 | 37.394 | 0.000 | |
| 龙祥岛 | 2.791 | <0.001 | 17.454 | 0.000 | |
| 马尾 | 2.593 | <0.01 | 10.597 | 0.000 | |
| 长乐 | 2.470 | <0.01 | 13.791 | 0.000 | |
| 连江 | 2.783 | <0.001 | 26.170 | 0.000 | |
| 合计 | 4.276 | <0.001 | 57.353 | 0.000 | |
| Cyt b | 延平 | -0.240 | >0.10 | 15.064 | 0.000 |
| 闽侯 | 2.183 | <0.05 | 34.509 | 0.000 | |
| 龙祥岛 | 0.996 | >0.10 | 18.303 | 0.000 | |
| 马尾 | 0.183 | >0.10 | 0.303 | 0.249 | |
| 长乐 | -0.395 | >0.10 | 24.696 | 0.000 | |
| 连江 | 2.113 | <0.05 | 12.244 | 0.000 | |
| 合计 | 3.190 | <0.01 | 44.516 | 0.000 | |
| 16S rRNA | 延平 | 2.182 | <0.05 | 34.125 | 0.000 |
| 闽侯 | 2.827 | <0.001 | 35.060 | 0.000 | |
| 龙祥岛 | 2.860 | <0.001 | 17.796 | 0.000 | |
| 马尾 | 2.795 | <0.001 | 24.312 | 0.000 | |
| 长乐 | 3.042 | <0.001 | 35.355 | 0.000 | |
| 连江 | 2.986 | <0.001 | 24.525 | 0.000 | |
| 合计 | 4.861 | <0.001 | — | 0.000 | |
表7 闽江6个不同河段河蚬COⅠ、Cyt b和16S rRNA基因的中性检验
Tab.7 Results of neutral test for C.fluminea populations in the 6 reaches of Minjiang River based on CO Ⅰ, Cyt b and 16S rRNA gene
| 基因 Gene | 群体 Population | Tajima’s D | Fu’s Fs | ||
|---|---|---|---|---|---|
| D | P | Fs | P | ||
| COⅠ | 延平 | 1.933 | >0.10 | 21.049 | 0.000 |
| 闽侯 | 2.831 | <0.001 | 37.394 | 0.000 | |
| 龙祥岛 | 2.791 | <0.001 | 17.454 | 0.000 | |
| 马尾 | 2.593 | <0.01 | 10.597 | 0.000 | |
| 长乐 | 2.470 | <0.01 | 13.791 | 0.000 | |
| 连江 | 2.783 | <0.001 | 26.170 | 0.000 | |
| 合计 | 4.276 | <0.001 | 57.353 | 0.000 | |
| Cyt b | 延平 | -0.240 | >0.10 | 15.064 | 0.000 |
| 闽侯 | 2.183 | <0.05 | 34.509 | 0.000 | |
| 龙祥岛 | 0.996 | >0.10 | 18.303 | 0.000 | |
| 马尾 | 0.183 | >0.10 | 0.303 | 0.249 | |
| 长乐 | -0.395 | >0.10 | 24.696 | 0.000 | |
| 连江 | 2.113 | <0.05 | 12.244 | 0.000 | |
| 合计 | 3.190 | <0.01 | 44.516 | 0.000 | |
| 16S rRNA | 延平 | 2.182 | <0.05 | 34.125 | 0.000 |
| 闽侯 | 2.827 | <0.001 | 35.060 | 0.000 | |
| 龙祥岛 | 2.860 | <0.001 | 17.796 | 0.000 | |
| 马尾 | 2.795 | <0.001 | 24.312 | 0.000 | |
| 长乐 | 3.042 | <0.001 | 35.355 | 0.000 | |
| 连江 | 2.986 | <0.001 | 24.525 | 0.000 | |
| 合计 | 4.861 | <0.001 | — | 0.000 | |

图8 基于16S rRNA基因闽江河种群的岐点分布
Fig.8 The mismatch distribution analysis ofC. fluminea population based on partial 16S rRNA gene sequences in Minjiang River
| [1] | 刘月英, 张文珍, 王跃先. 中国经济动物志:淡水软体动物[M]. 北京: 科学出版社, 1979. |
| [2] | 万德光. 药用动物学[M]. 上海: 上海科学技术出版社, 1993. |
| [3] | 李大命, 张彤晴, 关浩勇, 等. 基于线粒体Cyt b基因和D-loop区序列的高邮湖湖鲚(Coilia nasus)遗传多样性分析[J]. 淡水渔业, 2017, 47(6):3-8. |
| [4] | 李梦荣, 田雪, 庞小磊, 等. 基于线粒体COⅠ和Cyt b基因序列的6种锦鲤(Cyprinus carpio Koi)遗传多样性分析[J]. 淡水渔业, 2018, 48(3):13-18. |
| [5] | 欧阳美, 张晓宇, 张富铁, 等. 基于线粒体Cyt b基因序列的长江中上游草鱼野生和养殖群体遗传多样性比较研究[J]. 淡水渔业, 2021, 51(4):65-74. |
| [6] | 杨天燕, 孟玮, 马燕武, 等. 基于线粒体COⅠ和Cyt b基因序列对新疆两水系斑重唇鱼遗传结构的分析[J]. 淡水渔业, 2014, 44(4):41-47. |
| [7] | 郭易佳, 杨天燕, 孟玮, 等. 基于线粒体Cyt b基因的龙头鱼群体遗传结构分析[J]. 水生生物学报, 2019, 43(5):945-952. |
| [8] | 张帅, 李敏, 闫帅, 等. 基于线粒体Cyt b基因序列的棘头梅童鱼种群遗传结构[J]. 中国水产科学, 2021, 28(1):90-99. |
| [9] |
袁冬皓, 杨天燕, 孟玮, 等. 四种(鱚)属鱼类线粒体Cyt b基因的序列变异及系统发育研究[J]. 浙江农业学报, 2020, 32(1):35-42.
DOI |
| [10] |
Zhu C K, Li J, Xie S G, et al. Genetic diversity analysis of Asian clam Corbicula fluminea in the Hongze Lake based on mitochondrial cytochrome b gene[J]. Mitochondrial DNA Part A, 2018, 29(3):419-426.
DOI URL |
| [11] | 王剑平, 朱鹏飞, 王健, 等. 基于线粒体Cyt b基因序列的洞庭湖河蚬遗传多样性分析[J]. 水生态学杂志, 2018, 39(5):89-94. |
| [12] |
徐春燕, 庄之栋, 马超, 等. 基于COⅠ和16S rRNA基因片段鉴定厦门海域的仔稚鱼[J]. 渔业研究, 2021, 43(5):451-460.
DOI |
| [13] | 梁日深, 陈铭, 廖国威, 等. 基于16S rRNA与COⅠ基因40种石斑鱼亚科鱼类分子系统进化关系[J]. 海洋学报(中文版), 2020, 42(6):9-19. |
| [14] | 任桂静, 唐峰华, 马春艳, 等. 基于16S rRNA和COⅠ基因序列的柔鱼亚科系统进化关系探讨[J]. 海洋渔业, 2018, 40(5):522-530. |
| [15] | 陈双雅, 王嘉鹤, 陈伟玲, 等. 16S rRNA基因和COⅠ基因序列分析在石斑鱼物种鉴定中的应用[J]. 生物技术通报, 2012(10):124-130. |
| [16] | 陈信忠, 郭书林, 龚艳清, 等. 16S rRNA和CO Ⅰ基因条形码在12种观赏鱼种类鉴定中的应用[J]. 福建农业学报, 2016, 31(12):1267-1272. |
| [17] | 石林波, 张小燕, 汪雁, 等. 福建华溪蟹线粒体DNA、COⅠ和16S rRNA基因序列的遗传多样性[J]. 中国人兽共患病学报, 2013, 29(7):671-675. |
| [19] |
蒋芝华, 丁棒棒, 王熠, 等. 石首鱼科海洋鱼类DNA条形码的构建[J]. 核农学报, 2018, 32(4):673-680.
DOI |
| [20] | 王楠, 邢冉冉, 马聪聪, 等. DNA条形码技术在鲑科鱼类真伪鉴别中的应用[J]. 中国食品学报, 2020, 20(9):232-240. |
| [21] | 黄权, 蒋焯. 基于线粒体COⅠ和16S rRNA基因序列的虹鳟DNA条形码研究[J]. 吉林农业大学学报, 2022, 44(2):215-220. |
| [22] | 闫永斌, 葛玉双, 程起群, 等. 基于线粒体16S rRNA和COⅠ序列的江苏启东海域4种贝类遗传多样性分析[J]. 海洋渔业, 2022, 44(2):201-208. |
| [23] | 陈丽梅, 孔晓瑜, 喻子牛, 等. 3种蛏类线粒体16S rRNA和COⅠ基因片段的序列比较及其系统学初步研究[J]. 海洋科学, 2005, 29(8):27-32. |
| [24] | 孙超, 刘志鸿, 杨爱国, 等. 4种河蓝蛤线粒体COⅠ和16S rRNA基因序列的种间遗传分析[J]. 渔业科学进展, 2014, 35(1):82-90. |
| [25] | 毕春晴, 刘燕, 郭文靖, 等. 河蚬(Corbicula fluminea)对氧化石墨烯和全氟辛烷磺酸类物质(PFOS)联合胁迫的生理生化响应[J]. 北京大学学报(自然科学版), 2022, 58(4):721-729. |
| [26] | 韩鹏, 王勤, 陈清西. 河蚬软体部分营养成分分析及评价[J]. 厦门大学学报(自然科学版), 2007, 46(1):115-117. |
| [27] | 唐晟凯, 张彤晴, 崔晓翠, 等. 洪泽湖不同年龄河蚬营养成分的分析与评价[J]. 江苏农业科学, 2018, 46(18):196-199. |
| [28] | 王庆志, 常亚青. 大洋河河蚬的繁殖生物学研究[J]. 大连水产学院学报, 2010, 25(1):8-13. |
| [29] | 赵雪琳, 郑小东, 孙同秋, 等. 黄河三角洲河蚬(Corbicula fluminea)的繁殖生物学研究[J]. 海洋与湖沼, 2012, 43(5):1008-1015. |
| [30] | 吴丛迪, 张建琦, 夏思宇, 等. 洪泽湖河蚬繁殖高峰期的生物学研究[J]. 基因组学与应用生物学, 2020, 39(5):2028-2032. |
| [31] | 李大命, 张彤晴, 唐晟凯, 等. 洪泽湖野生河蚬(Corbicula fluminea)线粒体COⅠ基因序列的遗传多样性分析[J]. 渔业科学进展, 2015, 36(5):81-86. |
| [32] | 王剑平, 李德亮, 曾聪, 等. 捞刀河浏阳段河蚬的遗传多样性及生殖特征研究[J]. 水生生物学报, 2018, 42(5):913-918. |
| [33] | 蔡炜, 蔡永久, 龚志军, 等. 太湖河蚬时空格局[J]. 湖泊科学, 2010, 22(5):714-722. |
| [34] | 李德亮, 张婷, 肖调义, 等. 湖南省大通湖河蚬(Corbicula fluminea)现存量及其时空分布[J]. 湖泊科学, 2013, 25(5):743-748. |
| [35] | 张彤晴, 唐晟凯, 李大命, 等. 洪泽湖河蚬空间分布及资源量研究[J]. 江苏农业科学, 2017, 45(20):180-187. |
| [36] | 李天云, 孙凡, 黄圣彪, 等. 闽江某河段河蚬组织中多环芳烃和有机氯农药的蓄积特征[J]. 西南师范大学学报(自然科学版), 2007, 32(6):72-77. |
| [37] | 徐其建, 黄镇, 林岗. 凹线仙女蚬Cyt b基因片段序列分析及系统进化树初步构建[J]. 福建农业科技, 2020, 51(10):1-9. |
| [38] | Morton B. Polymorphism in Corbicula fluminea (Bivalvia:Corbiculoidea) from Hongkong[J]. Malacological Review, 1987, 20:105-127. |
| [39] |
Sousa R, Freire R, Rufino M, et al. Genetic and shell morphological variability of the invasive bivalve Corbicula fluminea (Mǜller,1774) in two Portuguese estuaries[J]. Estuarine,Coastal and Shelf Science, 2007, 74:166-174.
DOI URL |
| [40] | 王庆恒, 邓岳文, 杜晓东. 波纹巴非蛤Paphia undulata表型性状通径和回归分析[J]. 热带海洋学报, 2010, 29(5):132-135. |
| [41] | 张俊杰, 周浩郎, 邢永泽, 等. 红树蚬表型性状对秋季软体部重量的影响效果分析[J]. 广西科学, 2012, 19(4):384-386. |
| [42] | 李大命, 张彤晴, 唐晟凯, 等. 基于线粒体COⅠ序列的洪泽湖河蚬(Corbicula fluminea)遗传多样性和种群结构分析[J]. 海洋与湖沼, 2015, 46(6):1339-1346. |
| [43] |
Houki S, Yamada M, Honda T, et al. Origin and possible role of males in hermaphroditic androgenetic Corbicula clams[J]. Zoological Science, 2011, 28 (7):526-531.
DOI URL |
| [44] |
Tajima F. Statistical method for testing the neutral mutation hypothesis by DNA polymorphism[J]. Genetics, 1989, 123(3):585-595.
DOI PMID |
| [45] |
Fu Y X. Statistical tests of neutrality of mutations against population growth,hitchhiking and background selection[J]. Genetics, 1997, 147(2):915-925.
DOI PMID |
| [1] | 李昭楠, 李长忠, 保长虹, 贺彩霞, 金文杰, 陈艳霞. 基于DNA条形码技术的虹鳟分子鉴定[J]. 渔业研究, 2023, 45(4): 331-340. |
| [2] | 蒋飞 戴习林. 罗氏沼虾3个不同群体线粒体COⅠ基因序列变异及遗传多样性分析[J]. 渔业研究, 2023, 45(1): 8-13. |
| [3] | 杨子萍 李大命 刘燕山 杨家新. 基于Cyt b序列的太湖和洪泽湖翘嘴鲌遗传多样性和遗传结构分析[J]. 渔业研究, 2023, 45(1): 1-7. |
| [4] | 刘四光 张乐蒙 黄智伟 陈岚 王键 陈凯. 闽江河口区水体抗生素污染特征及风险评价[J]. 渔业研究, 2022, 44(5): 426-443. |
| [5] | 刘勇 马超 赵文武 翁祖桐 徐春燕 庄之栋 蔡建堤 谢少卿 沈长春. 闽江口及附近海域春夏季鱼类群落结构特征[J]. 渔业研究, 2022, 44(5): 467-476. |
| [6] | 赵天旸 石成春 谢蓉蓉 李家兵 江华 陈锦 刘继辉. 闽江流域近年主要水质指标变化趋势及污染识别[J]. 渔业研究, 2022, 44(4): 324-335. |
| [7] | 林建杰. 闽江口潮间带大型底栖动物群落基本特征分析[J]. 渔业研究, 2022, 44(1): 33-43. |
| [8] | 林建杰. 闽江口水环境主要理化因子时空分布特征研究[J]. 渔业研究, 2021, 43(6): 549-561. |
| [9] | 徐春燕 庄之栋 马超 刘勇 沈长春 蔡建堤 谢少卿. 基于COI和16S rRNA基因片段鉴定厦门海域的仔稚鱼[J]. 渔业研究, 2021, 43(5): 451-460. |
| [10] | 肖莹. 2008年闽江口海域叶绿素a时空分布及其与环境因子的相关性分析[J]. , 2014, 36(4): 271-277. |
| [11] | 林建杰. 闽江口海域海水中重金属的含量变化趋势研究[J]. 福建水产, 2013, 35(3): 203-210. |
| [12] | 巫旗生 曾志南 宋传福 宁岳 陈朴贤. 福建东山和广东阳江褐毛鲿养殖群体遗传多样性的AFLP分析[J]. 福建水产, 2012, 34(6): 435-439. |
| [13] | 陈月. 野生翘嘴红鲌的驯养及人工繁育试验[J]. 福建水产, 2012, 34(3): 231-235. |
| [14] | 宁岳 巫旗生 徐德华 郭金泉 曾志南 林向阳. 不同地理种群裸体方格星虫遗传结构及种群分化研究[J]. 福建水产, 2012, 34(2): 91-98. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||